| TBXT |
|---|
 |
| 識別子 |
|---|
| 記号 | TBXT, T, brachyury homolog (mouse), SAVA, TFT, T brachyury transcription factor, T-box transcription factor T, T |
|---|
| 外部ID | OMIM: 601397 MGI: 98472 HomoloGene: 2393 GeneCards: TBXT |
|---|
| 遺伝子の位置 (ヒト) |
|---|
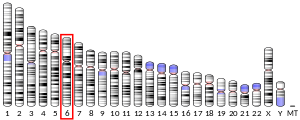 | | 染色体 | 6番染色体 (ヒト)[1] |
|---|
| | バンド | データ無し | 開始点 | 166,157,656 bp[1] |
|---|
| 終点 | 166,168,700 bp[1] |
|---|
|
| 遺伝子の位置 (マウス) |
|---|
 | | 染色体 | 17番染色体 (マウス)[2] |
|---|
| | バンド | データ無し | 開始点 | 8,653,255 bp[2] |
|---|
| 終点 | 8,661,328 bp[2] |
|---|
|
| 遺伝子オントロジー |
|---|
| 分子機能 | • RNA polymerase II cis-regulatory region sequence-specific DNA binding
• DNA結合
• sequence-specific DNA binding
• DNA-binding transcription factor activity
• transcription factor activity, RNA polymerase II distal enhancer sequence-specific binding
• DNA-binding transcription factor activity, RNA polymerase II-specific
|
|---|
| 細胞の構成要素 | • 細胞質
• クロマチン
• 細胞核
|
|---|
| 生物学的プロセス | • 体節形成
• cellular response to retinoic acid
• determination of heart left/right asymmetry
• regulation of transcription, DNA-templated
• SMAD protein signal transduction
• regulation of transcription by RNA polymerase II
• neural plate morphogenesis
• bone morphogenesis
• 解剖学的構造の形態形成
• heart morphogenesis
• notochord development
• signal transduction involved in regulation of gene expression
• negative regulation of transcription by RNA polymerase II
• BMP signaling pathway
• transcription, DNA-templated
• embryonic skeletal system development
• 脈管形成
• 多細胞個体の発生
• 生殖プロセス
• neural tube closure
• positive regulation of cell population proliferation
• 脊索
• post-anal tail morphogenesis
• canonical Wnt signaling pathway
• mesoderm migration involved in gastrulation
• 中胚葉の発生
• anterior/posterior axis specification, embryo
• penetration of zona pellucida
• primitive streak formation
• シグナル伝達
• anterior/posterior pattern specification
• positive regulation of transcription by RNA polymerase II
• negative regulation of DNA-binding transcription factor activity
|
|---|
| 出典:Amigo / QuickGO |
|
| オルソログ |
|---|
| 種 | ヒト | マウス |
|---|
| Entrez | | |
|---|
| Ensembl | | |
|---|
| UniProt | | |
|---|
RefSeq
(mRNA) | |
|---|
NM_001270484
NM_003181
NM_001366285
NM_001366286 |
| |
|---|
RefSeq
(タンパク質) | |
|---|
NP_001257413
NP_003172
NP_001353214
NP_001353215 |
| |
|---|
場所
(UCSC) | Chr 6: 166.16 – 166.17 Mb | Chr 6: 8.65 – 8.66 Mb |
|---|
| PubMed検索 | [3] | [4] |
|---|
| ウィキデータ |
|
ブラキウリ (英: Brachyury) はヒトではT 遺伝子にコードされたタンパク質である[5]。ブラキウリはTボックスファミリーに属する転写因子である。これまで調べられたすべての左右相称動物で見つかっており、刺胞動物にも存在している[6]。
歴史
Brachyury の変異は、1927年、Nadine Dobrovolskaïa-Zavadskaïa によってヘテロ接合体マウスにおける尾および仙骨の長さの変異として初めて記述された。ホモ接合体においてはbrachyury の変異は発生後10日目に中胚葉形成、および脊索分化の異常、前肢芽後側の構造欠損により致死性になる。Brachyury の名称はギリシャ語で短いを意味するbrakhus と尾を意味するoura より作られた。
ヒトおよびマウスのゲノム命名規則により、現在ではbrachyuryはTという名称を持つが、brachyury は発現タンパクの名称として現在も用いられている。
マウスのT 遺伝子は Bernhard Herrmann らによってクローンされ、436アミノ酸からなる胚の核内転写因子であることが明らかにされた[7]。Tは繰り返し様配列である TCACACCT にT-boxと呼ばれるN末端領域で結合する。T は現在、哺乳類では18種類が知られるT-box遺伝子群のうち初めに見つかった遺伝子である。
機能
Brachyury 遺伝子は左右相称動物において正中線を規定するという保存された機能を持ち [8]、これに伴って前後軸を形成する。この機能は脊索動物、および軟体動物で著名である[9]。この遺伝子の原始的な---少なくとも刺胞動物における---役割は、原口を形成することである.[6]。また、原腸陥入時に中胚葉を規定する[10]。中胚葉の形成と、中胚葉系への細胞分化にはこの遺伝子の発現が不可欠である。
発現
マウスではT は胚盤胞の内部細胞塊、続いて原始線条で発現する(ただし多くのマウス胚性幹細胞では見られない)。発生後期において発現は結節および脊索に限局される。アフリカツメガエル(Xenopus laevis )においてはXbra (Xenopus におけるT のホモログであり、近年は同じくt と呼ばれる)は原腸陥入前の帯域に発現し、中期原腸胚において原口および脊索に限局される。ゼブラフィッシュ(Danio rerio )におけるホモログはntl (no tail )である。
癌
ブラキウリの発現は脊椎内に残った脊索細胞の悪性腫瘍である脊索腫の確定診断マーカーである。また、生殖細胞におけるブラキウリの倍化は脊索腫が疑われる。Brachyury を含む染色体上の 6q27 領域が21例中6例で増加が見られ、一方欠失は見られなかった[11]。 ブラキウリは多くの多くの腫瘍で過剰発現が見られる。このタンパクは上皮間葉転換に寄与し、浸潤を促進する。
脚注
[脚注の使い方]
注釈
出典
- ^ a b c GRCh38: Ensembl release 89: ENSG00000164458 - Ensembl, May 2017
- ^ a b c GRCm38: Ensembl release 89: ENSMUSG00000062327 - Ensembl, May 2017
- ^ Human PubMed Reference:
- ^ Mouse PubMed Reference:
- ^ Edwards YH, Putt W, Lekoape KM, Stott D, Fox M, Hopkinson DA, Sowden J (March 1996). “The human homolog T of the mouse T(Brachyury) gene; gene structure, cDNA sequence, and assignment to chromosome 6q27”. Genome Res. 6 (3): 226–33. doi:10.1101/gr.6.3.226. PMID 8963900.
- ^ a b Scholz CB, Technau U (January 2003). “The ancestral role of Brachyury: expression of NemBra1 in the basal cnidarian Nematostella vectensis (Anthozoa)”. Dev. Genes Evol. 212 (12): 563–70. doi:10.1007/s00427-002-0272-x. PMID 12536320.
- ^ Herrmann BG, Labeit S, Poustka A, King TR, Lehrach H (February 1990). “Cloning of the T gene required in mesoderm formation in the mouse”. Nature 343 (6259): 617–22. doi:10.1038/343617a0. PMID 2154694.
- ^ Le Gouar, M.; Guillou, A.; Vervoort, M. (2004). “Expression of a SoxB and a Wnt2/13 gene during the development of the mollusc Patella vulgata.”. Development genes and evolution 214 (5): 250–256. doi:10.1007/s00427-004-0399-z. PMID 15034714.
- ^ Lartillot, N; Lespinet, O; Vervoort, M; Adoutte, A (2002). “Expression pattern of Brachyury in the mollusc Patella vulgata suggests a conserved role in the establishment of the AP axis in Bilateria.”. Development 129 (6): 1411–1421. PMID 11880350.
- ^ Marcellini, S.; Technau, U.; Smith, J.; Lemaire, P. (2003). “Evolution of Brachyury proteins: identification of a novel regulatory domain conserved within Bilateria”. Developmental Biology 260 (2): 352–361. doi:10.1016/S0012-1606(03)00244-6. PMID 12921737.
- ^ Vujovic S, Henderson S, Presneau N, Odell E, Jacques TS, Tirabosco R, Boshoff C, Flanagan AM (June 2006). “Brachyury, a crucial regulator of notochordal development, is a novel biomarker for chordomas”. J. Pathol. 209 (2): 157–65. doi:10.1002/path.1969. PMID 16538613. http://www.ncbi.nlm.nih.gov/pubmed/16538613.